Rashondenpopulaties genetisch in beeld gebracht
Onlangs verscheen een nieuwe studie over inteelt bij 112 hondenrassen (Dreger et al 2016). Hierin werd de inteelt op verschillende manieren bepaald en werden die manieren vervolgens met elkaar vergeleken. De insteek van het onderzoek was de genetica van complete rassen in beeld te brengen om zo het vinden van genetische afwijkingen te optimaliseren. De uitkomsten waren voor de wetenschap volgens de verwachtingen. Maar voor veel fokkers en kynologen zijn de cijfers waarschijnlijk verrassend en soms ronduit schokkend.
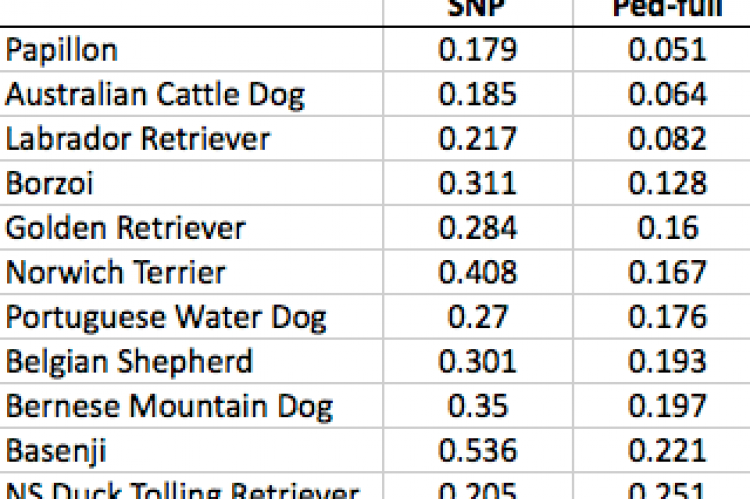
SNP
De afgelopen jaren is, met gebruikmaking van de gesloten populaties van honden, enorm veel vooruitgang geboekt op het gebied van studies naar ziektegevoeligheid, gedrag en morfologie en om dat te kunnen doen is het ook noodzakelijk om de populaties op zich te onderzoeken. Hierbij bleek al snel dat rasypische kenmerken voor dramatische gevolgen kunnen worden. Bij de onderzoeken werd allereerst gebruik gemaakt van SNP chip analyses. Het SNP (single nucleotide polymorphism) is een variatie op een specifieke plek in het DNA die het meest voorkomende variatietype is in het genoom. Met dit SNP, dat een individu kenmerkt, kan dus gekeken worden of dieren genetisch van elkaar verschillen. Hiermee wordt een DNA-identificatie gegeven op een populatieniveau. Omdat elk ras een unieke geschiedenis heeft zijn de resultaten hiervan wisselend.
COI en WGS
De tweede manier waarop de inteelt berekend werd was de geëigende methode: er werd gekeken naar het inteeltcoëfficiënt (COI) over vijf en tien generaties en over de gehele populatie van moment van invoering (het betreft hier een Amerikaans onderzoek).
Tenslotte werd er gebruik gemaakt van WGS (whole genome sequencing), een methode die in opkomst is omdat de andere methodes nogal eens gaten vertonen. Bij WGS wordt gekeken naar het totale genetische paket van de hond. WGS is voor de wetenschap interessant vanwege de enorme variatie die we zien bij honden wat betreft hun uiterlijke verschijning. Uit deze onderzoeken kwamen resultaten die de wetenschap niet verbaasden maar die vele fokkers en kynologen als schokkend zullen ervaren. Dachten we nog aardig veilig te zitten? Helaas is dat niet het geval. Bij de 112 onderzochte rassen bleek alleen de Nova Scotia Duck Tolling Retriever bij de COI-berekening iets hoger uit te komen dan bij de SNP. Bij alle andere rassen gaf de SNP schrikbarend veel hogere waardes aan dan de COI-berekening.
Bij de totale berekeningen zien we in de overzichtstabellen dat de Noorse Lundehund, de Bullterrier en de Basenji veruit het hoogste scoren. Van de Noorse Lundehund zijn de problemen bekend. In dat ras wordt ook hard gewerkt aan een manieren om vers genetisch materiaal in te voeren en dat is goed want er is al jaren sprake van inteeltdepressie en ziekte. We zien de Schotse collie en de Kromfohrlander ook hoog in de lijst staan, en ook bij deze rassen wordt momenteel gewerkt aan oplossingen. Wie zich realiseert dat alleen een rasgemiddeld COI van 0,5 toelaatbaar is om de genetische variatie gezond te houden, ziet dat er in de onderzochte 112 rassen slechts één ras is dat hier nog enigszins bij in de buurt komt: de Sloughi zit gemiddeld rond de 5%. Te hoog, maar vergeleken met andere rassen nog acceptabel.
Effectieve populatie
De effectieve populatiegrootte is het aantal dieren dat effectief wordt ingezet voor de fokkerij. De gedachte was dat deze getallen per ras sterk zouden verschillen omdat elk ras een unieke geschiedenis kent. Met behulp van SNP werd berekend hoe sterk het aantal per ras gedaald was. Uit deze onderzoeken bleek duidelijk dat men gebruik is gaan maken van steeds minder fokdieren per ras. Omdat de stijging niet kan komen doordat teven steeds meer nesten krijgen is er maar één verklaring: reuen geven steeds meer nesten per dier. Hierdoor ontstaan er bottlenecks in populaties, en wordt het risico op problemen vergroot.
Dit onderzoek betreft Amerikaanse populaties en zal daarom in details afwijken van Nederlandse en Europese populaties, maar de essentie is gelijk: de genetische diversiteit is sterk aan het dalen. Met alle gevolgen van dien. Met de technologie en kennis van dit moment is het zeker mogelijk hierop in te grijpen. Gelukkig wordt dat steeds meer algemeen aanvaard. Steeds meer rassen ondernemen actie. We houden u op de hoogte.
bron
Onderzoeksartikel Dreger et al 2016
Carol Beuchat Inteelt rashonden in beeld met DNA